Análisis filogenético del virus del chikungunya en Colombia: evidencia de selección purificadora en el gen E1
Resumen
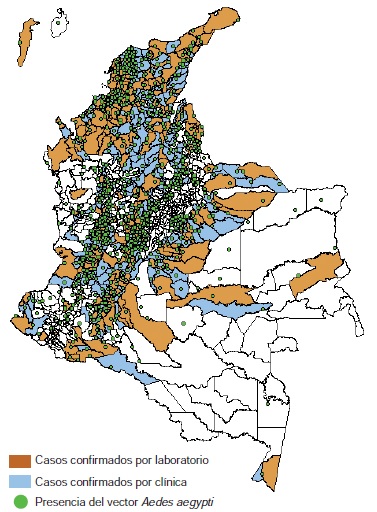
Introducción. El virus del chikungunya, perteneciente al género Alphavirus de la familia Togaviridae, es un virus ARN de 11,8 kb, de cadena sencilla y polaridad positiva, transmitido por Aedes spp. Se han identificado tres genotipos a nivel mundial: el de Asia, el del este-centro-sur de África (East/Central/South African, ECSA) y el de África occidental (West African, WA). La fiebre del chikungunya es una enfermedad febril aguda, acompañada principalmente de inflamación en las articulaciones y erupción cutánea. Después de su aparición en las Américas en el 2013, los primeros casos en Colombia ocurrieron en septiembre de 2014 y hasta junio del 2015 se habían notificado 399.932 casos.
Objetivo. Identificar el genotipo o los genotipos responsables de la primera epidemia por el virus del chikungunya en Colombia y la variabilidad genética asociada a su dispersión en el territorio nacional.
Materiales y métodos. Se seleccionaron muestras de suero de pacientes con síntomas indicativos de fiebre del chikungunya durante 2014 y 2015. Se hizo una transcripción inversa seguida de reacción en cadena de la polimerasa del gen E1, así como su secuenciación, análisis filogenético y análisis de evolución adaptativa.
Resultados. Se demostró la presencia exclusiva del genotipo de Asia en Colombia. Se registró un promedio de 0,001 sustituciones de bases por sitio, una identidad de 99,7 a 99,9 % en los nucleótidos y de 99,9 % en los aminoácidos entre las secuencias colombianas y las secuencias de las Américas. Los análisis de evolución adaptativa indicaron una fuerte selección purificadora en el gen E1.
Conclusiones. Se determinó la circulación del genotipo de Asia del virus del chikungunya como la causa de la primera epidemia en Colombia. Es necesario continuar con la vigilancia de genotipos, con el fin de detectar posibles cambios en la epidemiología, la eficacia (fitness) viral y la patogenia del virus.
Descargas
Referencias bibliográficas
Powers AM. Chikungunya. Clin Lab Med. 2010;30:209-19. http://dx.doi.org/10.1016/j.cll.2009.10.003
Knipe D, Howley P. Field’s Virology. Sixth edition. Philadelphia: Lippincott Williams & Wilkins; 2013. p. 651-86.
Ross RW. The Newala epidemic. III. The virus: Isolation, pathogenic properties and relationship to the epidemic. J Hyg (Lond). 1956;54:177-91.
Dupuis-Maguiraga L, Noret M, Brun S, Le Grand R, Gras G, Roques P. Chikungunya disease: Infection-associated markers from the acute to the chronic phase of arbovirus-induced arthralgia. PLoS Negl Trop Dis. 2012;6:e1446. http://dx.doi.org/10.1371/journal.pntd.0001446
Rougeron V, Sam IC, Caron M, Nkoghe D, Leroy E, Roques P. Chikungunya, a paradigm of neglected tropical disease that emerged to be a new health global risk. J Clin Virol. 2015;64:144-52. http://dx.doi.org/10.1016/j.jcv. 2014.08.032
Burt FJ, Rolph MS, Rulli NE, Mahalingam S, Heise MT. Chikungunya: A re-emerging virus. Lancet. 2012;379:662-71. http://dx.doi.org/10.1016/s0140-6736(11)60281-x
Weaver SC. Arrival of chikungunya virus in the new world: Prospects for spread and impact on public health. PLoS Negl Trop Dis. 2014;8:e2921. http://dx.doi.org/10.1371/journal.pntd.0002921
Mowatt L, Jackson ST. Chikungunya in the Caribbean: An epidemic in the making. Infect Dis Ther. 2014;3:63-8. http://dx.doi.org/10.1007/s40121-014-0043-9
Morrison TE. Reemergence of chikungunya virus. J Virol. 2014;88:11644-7. http://dx.doi.org/10.1128/jvi.01432-14
Instituto Nacional de Salud. Boletín epidemiológico semanal. Semana epidemiológica número 25 de 2015. Fecha de consulta: 15 de julio de 2015. Disponible en: http://www.ins.gov.co/boletin-epidemiologico/Paginas/default.aspx
Lo Presti A, Lai A, Cella E, Zehender G, Ciccozzi M. Chikungunya virus, epidemiology, clinics and phylogenesis: A review. Asian Pac J Trop Med. 2014;7:925-32. http://dx.doi.org/10.1016/s1995-7645(14)60164-4
Powers AM, Brault AC, Tesh RB, Weaver SC. Re-emergence of Chikungunya and O’nyong-nyong viruses: Evidence for distinct geographical lineages and distant evolutionary relationships. J Gen Virol. 2000;81:471-9. http://dx.doi.org/10.1099/0022-1317-81-2-471
Tsetsarkin KA, Chen R, Sherman MB, Weaver SC. Chikungunya virus: Evolution and genetic determinants of emergence. Curr Opin Virol. 2011;1:310-7. http://dx.doi.org/10.1016/j.coviro.2011.07.004
Volk SM, Chen R, Tsetsarkin KA, Adams AP, García TI, Sall AA, et al. Genome-scale phylogenetic analyses of chikungunya virus reveal independent emergences of recent epidemics and various evolutionary rates. J Virol. 2010;84:6497-504. http://dx.doi.org/10.1128/jvi.01603-09
Lo Presti A, Ciccozzi M, Cella E, Lai A, Simonetti FR, Galli M, et al. Origin, evolution, and phylogeography of recent epidemic CHIKV strains. Infect Genet Evol. 2012;12:392-8. http://dx.doi.org/10.1016/j.meegid.2011.12.015
Leparc-Goffart I, Nougairede A, Cassadou S, Prat C, de Lamballerie X. Chikungunya in the Americas. Lancet. 2014;383:514. http://dx.doi.org/10.1016/s0140-6736(14) 60185-9
Nunes MR, Faria NR, de Vasconcelos JM, Golding N, Kraemer MU, de Oliveira LF, et al. Emergence and potential for spread of Chikungunya virus in Brazil. BMC Med. 2015;13:102. http://dx.doi.org/10.1186/s12916-015-0348-x
Lanciotti RS, Kosoy OL, Laven JJ, Panella AJ, Vélez JO, Lambert AJ, et al. Chikungunya virus in US travelers returning from India, 2006. Emerg Infect Dis. 2007;13:764-7. http://dx.doi.org/10.3201/eid1305.070015
Larkin MA, Blackshields G, Brown NP, Chenna R, McGettigan PA, McWilliam H, et al. Clustal W and Clustal X version 2.0. Bioinformatics. 2007;23(21):2947-8. http://dx.doi.org/10.1093/bioinformatics/btm404
Darriba D, Taboada GL, Doallo R, Posada D. jModelTest 2: more models, new heuristics and parallel computing. Nat Methods. 9. United States2012. p. 772. http://dx.doi.org/10.1038/nmeth.2109
Huelsenbeck JP, Ronquist F. MRBAYES: Bayesian inference of phylogenetic trees. Bioinformatics. 2001;17(8): 754-5.
Tamura K, Stecher G, Peterson D, Filipski A, Kumar S. MEGA6: Molecular Evolutionary Genetics Analysis version 6.0. Mol Biol Evol. 2013;30(12):2725-9. http://dx.doi.org/10. 1093/molbev/mst197
Tajima F. Statistical method for testing the neutral mutation hypothesis by DNA polymorphism. Genetics. 1989;123(3): 585-95.
Fu YX, Li WH. Statistical tests of neutrality of mutations. Genetics. 1993;133(3):693-709.
Librado P, Rozas J. DnaSP v5: a software for comprehensive analysis of DNA polymorphism data. Bioinformatics. 2009;25(11):1451-2. http://dx.doi.org/10. 1093/bioinformatics/btp187
Pond SL, Frost SD. Datamonkey: rapid detection of selective pressure on individual sites of codon alignments. Bioinformatics. 2005;21(10):2531-3. http://dx.doi.org/10. 1093/bioinformatics/bti320
Instituto Nacional de Salud. IQEN Informe Quincenal Epidemiológico Nacional. Transmisión autóctona de Chikungunya en Colombia. 2014;19:311-38. Fecha de consulta: 6 de julio de 2015. Disponible en: http://www.ins.gov.co/iqen/Paginas/default.aspx
Groot H. Estudio sobre virus transmitidos por artrópodos en Colombia. Revista de la Academia Colombiana de Ciencias Exactas, Físicas y Naturales. 1964;12:197-217.
Powers AM, Brault AC, Shirako Y, Strauss EG, Kang W, Strauss JH, et al. Evolutionary relationships and systematics of the Alphaviruses. J Virol. 2001;75:10118-31. http://dx.doi.org/10.1128/jvi.75.21.10118-10131.2001
Mesa F, Cárdenas J, Villamil L. Las encefalitis equinas en la salud pública. Bogotá: UNAL; 2005. p. 1-124.
Instituto Nacional de Salud. Boletín epidemiológico semanal. Semana epidemiológica número 19 de 2015. Fecha de consulta: 15 de julio de 2015. Disponible en: http://www.ins.gov.co/boletin-epidemiologico/Paginas/default.aspx.
Instituto Nacional de Salud. Boletín epidemiológico semanal. 2014 - 2015. Fecha de consulta: 15 de julio de 2015. Disponible en: http://www.ins.gov.co/boletin-epidemiologico/Paginas/default.aspx.
Weaver SC, Rico-Hesse R, Scott TW. Genetic diversity and slow rates of evolution in New World alphaviruses. Curr Top Microbiol Immunol. 1992;176:99-117.
Tsetsarkin KA, Vanlandingham DL, McGee CE, Higgs S. A single mutation in chikungunya virus affects vector specificity and epidemic potential. PLoS Pathog. 2007;3:e201. http://dx.doi.org/10.1371/journal.ppat.0030201
Weaver SC, Brault AC, Kang W, Holland JJ. Genetic and fitness changes accompanying adaptation of an arbovirus to vertebrate and invertebrate cells. J Virol. 1999;73:4316-26.
Schuffenecker I, Iteman I, Michault A, Murri S, Frangeul L, Vaney MC, et al. Genome microevolution of chikungunya viruses causing the Indian Ocean outbreak. PLoS Med. 2006;3:e263. http://dx.doi.org/10.1371/journal.pmed.0030263
Vazeille M, Moutailler S, Coudrier D, Rousseaux C, Khun H, Huerre M, et al. Two Chikungunya isolates from the outbreak of La Réunion (Indian Ocean) exhibit different patterns of infection in the mosquito, Aedes albopictus. PLoS One. 2007;2:e1168. http://dx.doi.org/10.1371/journal.pone.0001168
Algunos artículos similares:
- Andrés Gómez-Palacio, Juan Suaza-Vasco, Sandra Castaño, Omar Triana, Sandra Uribe, Infección de Aedes albopictus (Skuse, 1894) con el genotipo asiático-americano del virus del dengue serotipo 2 en Medellín y su posible papel como vector del dengue en Colombia , Biomédica: Vol. 37 Núm. Sup. 2 (2017): Suplemento 2, Entomología médica, 2017
- Myrtha Arango, Elizabeth Castañeda, Clara Inés Agudelo, Catalina De Bedout, Carlos Andrés Agudelo, Angela Tobón, Melva Linares, Yorlady Valencia, Ángela Restrepo, The Colombian Histoplasmosis Study Group, Histoplasmosis en Colombia: resultados de la encuesta nacional, 1992-2008 , Biomédica: Vol. 31 Núm. 3 (2011)
- José Joaquín Carvajal, Nildimar Alves Honorio, Silvia Patricia Díaz, Edinso Rafael Ruiz, Jimmy Asprilla, Susanne Ardila, Gabriel Parra-Henao, Detección de Aedes albopictus (Skuse) (Diptera: Culicidae) en el municipio de Istmina, Chocó, Colombia , Biomédica: Vol. 36 Núm. 3 (2016)
- Lucero Rengifo, Duverney Gaviria, Herman Serrano, Polimorfismos del gen ApoE en individuos con síndrome de Down y sus progenitores en una población colombiana , Biomédica: Vol. 32 Núm. 2 (2012)
- María Claudia Atencia, María de Jesús Pérez, María Cristina Jaramillo, Sandy Milena Caldera, Suljey Cochero, Eduar Elías Bejarano, Primer reporte de la mutación F1534C asociada con resistencia cruzada a DDT y piretroides en Aedes aegypti en Colombia , Biomédica: Vol. 36 Núm. 3 (2016)
- Marylin Hidalgo, Claudia Santos, Carolina Duarte, Elizabeth Castañeda, Clara Inés Agudelo, Incremento de la resistencia a eritromicina de Streptococcus pneumoniae, Colombia, 1994-2008 , Biomédica: Vol. 31 Núm. 1 (2011)
- Andrés Javier Quiroga, Diana Marcela Cittelly, María Mercedes Bravo, Frecuencia de los genotipos babA2, oipA y cagE de Helicobacter pylori en pacientes colombianos con enfermedades gastroduodenales. , Biomédica: Vol. 25 Núm. 3 (2005)
- Pablo Chaparro, Edison Soto, Julio Padilla, Daniel Vargas, Estimación del subregistro de casos de paludismo en diez municipios de la costa del Pacífico nariñense durante 2009 , Biomédica: Vol. 32 (2012): Suplemento 1, Malaria
- Alberto Gómez, Sandra J. Ávila, Ignacio Briceño, De genotipos e isonimias: análisis de correlación entre el apellido y el patrimonio genético heredado en el cromosoma Y en la población de tres departamentos del suroccidente colombiano , Biomédica: Vol. 28 Núm. 3 (2008)
- Yesika del Carmen Rojas, Helena Brochero, Hallazgo de Aedes aegypti (Linnaeus 1762), en el casco urbano del corregimiento de La Pedrera, Amazonas, Colombia , Biomédica: Vol. 28 Núm. 4 (2008)
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |